Stop kodon: Perbedaan antara revisi
Tidak ada ringkasan suntingan Tag: Suntingan visualeditor-wikitext |
Tidak ada ringkasan suntingan Tag: Suntingan visualeditor-wikitext |
||
| Baris 1: | Baris 1: | ||
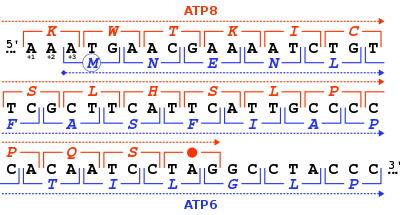
[[File:Homo sapiens-mtDNA~NC 012920-ATP8+ATP6 Overlap.svg|thumb|right|400px|Stop kodon (titik merah) dari mitokondria DNA manusia gen ''MT-ATP8'', dan start Kodon (lingkaran biru) pada gen ''MT-ATP6''. Untuk setiap triplet nukleotida (tanda kurung siku), asam amino yang sesuai diberikan (kode satu huruf), baik di +1 di dalam bingkai untuk ''MT-ATP8'' (warna merah) atau di +3 bingkai untuk ''MT-ATP6'' (warna biru). Di wilayah [[genom]] ini, dua gen [[Gen|tumpang tindih]].]] |
[[File:Homo sapiens-mtDNA~NC 012920-ATP8+ATP6 Overlap.svg|thumb|right|400px|Stop kodon (titik merah) dari mitokondria DNA manusia gen ''MT-ATP8'', dan start Kodon (lingkaran biru) pada gen ''MT-ATP6''. Untuk setiap triplet nukleotida (tanda kurung siku), asam amino yang sesuai diberikan (kode satu huruf), baik di +1 di dalam bingkai untuk ''MT-ATP8'' (warna merah) atau di +3 bingkai untuk ''MT-ATP6'' (warna biru). Di wilayah [[genom]] ini, dua gen [[Gen|tumpang tindih]].]] |
||
'''Stop kodon''' ([[Bahasa Inggris|Inggris]]: ''Stop Codon'') atau disebut juga "Terminasi kodon" atau "Penghentian kodon", di dalam [[Molekuler|molekuler biologi]] merupakan sebuah [[Kode genetik]] atau [[Kodon|kodon]] ([[nukleotida]] triplet dalam [[mRNA|messenger RNA]]) yang menandakan penghentian proses [[Translasi (biologi)|translasi]] pada [[protein]].<ref>{{cite book|vauthors=((Griffiths AJF)), Miller JH, Suzuki DT, Lewontin RC, Gelbart WM | title=An Introduction to Genetic Analysis| year=2000| publisher=W.H. Freeman and Company |chapterurl=https://www.ncbi.nlm.nih.gov/books/bv.fcgi?rid=iga.section.1845#1872 |chapter=Chapter 10 (Molecular Biology of Gene Function): Genetic code: Stop codons}}</ref> Kebanyakan kodon dalam messenger RNA ([[mRNA]]) berhubungan dengan penambahan [[asam amino]] ke rantai [[polipeptida]] yang tumbuh, dan pada akhirnya dapat menjadi protein. Stop kodon akan memberi sinyal penghentian proses ini dengan mengikat [[faktor pelepasan]], yang menyebabkan sub-unit [[ribosom|ribosom]] terlepas, melepaskan rantai [[asam amino]]. |
'''Stop kodon''' atau '''Kodon stop''' ([[Bahasa Inggris|Inggris]]: ''Stop Codon'') atau disebut juga "Terminasi kodon" atau "Penghentian kodon", di dalam [[Molekuler|molekuler biologi]] merupakan sebuah [[Kode genetik]] atau [[Kodon|kodon]] ([[nukleotida]] triplet dalam [[mRNA|messenger RNA]]) yang menandakan penghentian proses [[Translasi (biologi)|translasi]] pada [[protein]].<ref>{{cite book|vauthors=((Griffiths AJF)), Miller JH, Suzuki DT, Lewontin RC, Gelbart WM | title=An Introduction to Genetic Analysis| year=2000| publisher=W.H. Freeman and Company |chapterurl=https://www.ncbi.nlm.nih.gov/books/bv.fcgi?rid=iga.section.1845#1872 |chapter=Chapter 10 (Molecular Biology of Gene Function): Genetic code: Stop codons}}</ref> Kebanyakan kodon dalam messenger RNA ([[mRNA]]) berhubungan dengan penambahan [[asam amino]] ke rantai [[polipeptida]] yang tumbuh, dan pada akhirnya dapat menjadi protein. Stop kodon akan memberi sinyal penghentian proses ini dengan mengikat [[faktor pelepasan]], yang menyebabkan sub-unit [[ribosom|ribosom]] terlepas, melepaskan rantai [[asam amino]]. |
||
== Properti == |
== Properti == |
||
| Baris 99: | Baris 99: | ||
=== Translasi === |
=== Translasi === |
||
Tahun 2007, kodon UGA diidentifikasi sebagai kodon yang mengkode [[Selenosistein|selenosistein]] (Sec) dan ditemukan pula di 25 [[Selenoprotein|selenoprotein]] yang terdapat pada situs aktif [[protein]]. Kodon UAG dapat juga diterjemahkan ke dalam [[Pirolisis|pirolisis]] (Pyl) dengan cara yang sama, dan terjemahan kodon ini diaktifkan oleh kedekatan elemen SECIS (''SElenoCysteine Incorporation Sequence'') atau Urutan Penggabungan SElenoCysteine.<ref>{{cite journal |pages=775–806 |doi=10.1089/ars.2007.1528 |title=From Selenium to Selenoproteins: Synthesis, Identity, and Their Role in Human Health |year=2007 |last1=Papp |first1=Laura Vanda |last2=Lu |first2=Jun |last3=Holmgren |first3=Arne |last4=Khanna |first4=Kum Kum |journal=Antioxidants & Redox Signaling |volume=9 |issue=7 |pmid=17508906|s2cid=38176932 |url=https://semanticscholar.org/paper/86118b8c1a6149e0e22d6184bf59ee2b446563e5 }}</ref> |
Tahun 2007, kodon UGA diidentifikasi sebagai kodon yang mengkode [[Selenosistein|selenosistein]] (Sec) dan ditemukan pula di 25 [[Selenoprotein|selenoprotein]] yang terdapat pada situs aktif [[protein]]. Kodon UAG dapat juga diterjemahkan ke dalam [[Pirolisis|pirolisis]] (Pyl) dengan cara yang sama, dan terjemahan kodon ini diaktifkan oleh kedekatan elemen SECIS (''SElenoCysteine Incorporation Sequence'') atau Urutan Penggabungan SElenoCysteine.<ref>{{cite journal |pages=775–806 |doi=10.1089/ars.2007.1528 |title=From Selenium to Selenoproteins: Synthesis, Identity, and Their Role in Human Health |year=2007 |last1=Papp |first1=Laura Vanda |last2=Lu |first2=Jun |last3=Holmgren |first3=Arne |last4=Khanna |first4=Kum Kum |journal=Antioxidants & Redox Signaling |volume=9 |issue=7 |pmid=17508906|s2cid=38176932 |url=https://semanticscholar.org/paper/86118b8c1a6149e0e22d6184bf59ee2b446563e5 }}</ref> |
||
=== Distribusi genomik === |
|||
Pembagian stop kodon dalam [[genom]] suatu [[organisme]] tidak terjadi secara acak dan bisa jadi berkorelasi dengan [[konten GC]].<ref>{{Cite journal|title=Stop codons in bacteria are not selectively equivalent|doi=10.1186/1745-6150-7-30|journal=Biology Direct|pmid=22974057|pmc=3549826|year=2012|volume=7|pages=30|vauthors=Povolotskaya IS, Kondrashov FA, Ledda A, Vlasov PK}}</ref><ref>{{cite journal |pages=775–806 |doi=10.1074/jbc.M114.606632 |title=Comprehensive Analysis of Stop Codon Usage in Bacteria and Its Correlation with Release Factor Abundance|year=2014 |last1=Korkmaz|first1=Gürkan |last2=Holm |first2=Mikael |last3=Wiens|first3=Tobias |last4=Sanyal|first4=Suparna |journal=The Journal of Biological Chemistry |volume=289 |issue=44 |pmid=25217634 |pmc=4215218}}</ref> Sebagai contoh, genom K-12 ''E. coli'' mengandung 2705 TAA (63%), 1257 TGA (29%), dan 326 TAG (8%) stop kodon (konten GC 50.8%).<ref>{{cite web |title=''Escherichia coli'' str. K-12 substr. MG1655, complete genome [Genbank Accession Number: U00096] |publisher=NCBI |work=GenBank |url=https://www.ncbi.nlm.nih.gov/nuccore/U00096 |accessdate=2020-11-23}}</ref> |
|||
[[Substrat]] untuk stop kodon faktor pelepasan 1 atau faktor pelepasan 2 memiliki korelasi dengan kelimpahan stop kodon.<ref>{{cite journal |pages=775–806 |doi=10.1074/jbc.M114.606632 |title=Comprehensive Analysis of Stop Codon Usage in Bacteria and Its Correlation with Release Factor Abundance|year=2014 |last1=Korkmaz|first1=Gürkan |last2=Holm |first2=Mikael |last3=Wiens|first3=Tobias |last4=Sanyal|first4=Suparna |journal=The Journal of Biological Chemistry |volume=289 |issue=44 |pmid=25217634 |pmc=4215218}}</ref> Skala besar studi tentang bakteri dengan berbagai kandungan GC menjelaskan bahwa frekuensi terjadinya TAA memiliki korelasi negatif dengan konten GC sementara frekuensi terjadinya TGA memiliki korelasi positif dengan konten GC, dan frekuensi terjadinya stop kodon TAG, menjadi paling sedikit dipakai dalam genom, dan tidak dipengaruhi oleh konten GC.<ref>{{cite journal |pages=6718–6725 |doi=10.1128/JB.00682-08 |title= Role of Premature Stop Codons in Bacterial Evolution |year=2008 |last1=Wong|first1=Tit-Yee |last2= Fernandes |first2=Sanjit |last3=Sankhon|first3=Naby |last4=Leong|first4=Patrick P | last5=Kuo|first5=Jimmy |last6=Liu|first6=Jong-Kang |journal=Journal of Bacteriology |volume=190 |issue=20 |pmid=18708500 |pmc=2566208}}</ref> |
|||
=== Pengenalan === |
|||
Pengenalan stop kodon terhadap [[bakteri]] telah dikaitkan dengan sebutan 'antikodon tripeptida',<ref>{{cite journal |doi=10.1038/35001115 |title= A tripeptide 'anticodon' deciphers stop codons in messenger RNA |year=1999 |last1=Ito|first1=Koichi |last2= Uno|first2=Makiko |last3=Nakamura|first3=Yoshikazu |journal=Nature |volume=403 |issue= 6770 |pages= 680–684 |pmid=10688208 |s2cid= 4331695 }}</ref> motif [[asam amino]] yang sangat dilestarikan di RF1 (PxT) dan RF2 (SPF). Walaupun hal ini telah didukung oleh sebuah studi struktural, namun terbukti bahwa [[hipotesis]] antikodon tripeptida merupakan sebuah penyederhanaan yang berlebihan.<ref>{{cite journal |doi=10.1074/jbc.M117.785238 |title= R213I mutation in release factor 2 (RF2) is one step forward for engineering an omnipotent release factor in bacteria ''Escherichia coli''|year=2017 |last1=Korkmaz|first1=Gürkan |last2= Sanyal|first2=Suparna |journal=Journal of Biological Chemistry|volume=292 |issue= 36|pages= 15134–15142|pmid=28743745 |pmc=5592688}}</ref> |
|||
== Sistem pemberian istilah == |
|||
Secara historis, stop kodon memiliki beragam nama yang berbeda, dan semuanya memiliki kaitan dengan kelas [[mutan]] yang berbeda namun semuanya berperilaku sama. Mutan ini terlebih dahulu diisolasi dalam [[bakteriofag]] ([[Enterobacteria phage T4|T4]] dan [[Lambda phage | lambda]]), [[virus]] yang menginfeksi bakteri ''[[Escherichia coli]]''. Mutasi pada gen [[virus]] akan melemahkan kemampuan infeksi, dan ada kemungkinan akan menciptakan virus yang mampu menginfeksi dan tumbuh hanya dalam [[varietas]] ''E. coli'' tertentu. |
|||
== Referensi == |
== Referensi == |
||
Revisi per 23 November 2020 13.19
Stop kodon atau Kodon stop (Inggris: Stop Codon) atau disebut juga "Terminasi kodon" atau "Penghentian kodon", di dalam molekuler biologi merupakan sebuah Kode genetik atau kodon (nukleotida triplet dalam messenger RNA) yang menandakan penghentian proses translasi pada protein.[1] Kebanyakan kodon dalam messenger RNA (mRNA) berhubungan dengan penambahan asam amino ke rantai polipeptida yang tumbuh, dan pada akhirnya dapat menjadi protein. Stop kodon akan memberi sinyal penghentian proses ini dengan mengikat faktor pelepasan, yang menyebabkan sub-unit ribosom terlepas, melepaskan rantai asam amino.
Properti
Standar kodon
Dalam kode genetik standar, ada tiga jenis kodon terminasi yang berbeda, yakni:
| Kodon | Kode Standar (Translasi tabel 1) |
Nama | ||
|---|---|---|---|---|
| DNA | RNA | |||
| TAG | UAG | STOP = Ter (*) | "amber" | |
| TAA | UAA | STOP = Ter (*) | "ochre" | |
| TGA | UGA | STOP = Ter (*) | "opal" (atau "umber") | |
Stop kodon alternatif
Terdapat variasi pada kode genetik standar, dan stop kodon alternatif yang telah ditemukan dalam genom mitokondria dari vertebrate,[2] Scenedesmus obliquus,[3] dan Thraustochitrid.[4]
| Kode Genetik | Tabel Translasi |
Kodon | Translasi dengan kode ini |
Translasi standar | ||||
|---|---|---|---|---|---|---|---|---|
| DNA | RNA | |||||||
| Vertebrate mitochondrial | 2 | AGA | AGA | STOP = Ter (*) | Arg (R) | |||
| AGG | AGG | STOP = Ter (*) | Arg (R) | |||||
| Scenedesmus obliquus mitochondrial | 22 | TCA | UCA | STOP = Ter (*) | Ser (S) | |||
| Thraustochytrium mitochondrial | 23 | TTA | UUA | STOP = Ter (*) | Leu (L) | |||
| sifat biokimia Amino-acid | Nonpolar | Polar | Basic | Acidic | Penghentian: stop kodon |
Penugasan ulang stop kodon
Kode genetik inti fleksibel seperti yang diilustrasikan oleh varian kode genetik, akan menugaskan kembali stop kodon standar menjadi asam amino.[5]
| Kode genetik | Tabel translasi |
Kodon | Syarat translasi |
Standar translasi | ||||
|---|---|---|---|---|---|---|---|---|
| DNA | RNA | |||||||
| Nuklir Karaorelict | 27 | TGA | UGA | Ter (*) | or | Trp (W) | Ter (*) | |
| Nuklir Condylostoma | 28 | TAA | UAA | Ter (*) | or | Gln (Q) | Ter (*) | |
| TAG | UAG | Ter (*) | or | Gln (Q) | Ter (*) | |||
| TGA | UGA | Ter (*) | or | Trp (W) | Ter (*) | |||
| Nuklir Blastocrithidia | 31 | TAA | UAA | Ter (*) | or | Glu (E) | Ter (*) | |
| TAG | UAG | Ter (*) | or | Glu (E) | Ter (*) | |||
Translasi
Tahun 2007, kodon UGA diidentifikasi sebagai kodon yang mengkode selenosistein (Sec) dan ditemukan pula di 25 selenoprotein yang terdapat pada situs aktif protein. Kodon UAG dapat juga diterjemahkan ke dalam pirolisis (Pyl) dengan cara yang sama, dan terjemahan kodon ini diaktifkan oleh kedekatan elemen SECIS (SElenoCysteine Incorporation Sequence) atau Urutan Penggabungan SElenoCysteine.[6]
Distribusi genomik
Pembagian stop kodon dalam genom suatu organisme tidak terjadi secara acak dan bisa jadi berkorelasi dengan konten GC.[7][8] Sebagai contoh, genom K-12 E. coli mengandung 2705 TAA (63%), 1257 TGA (29%), dan 326 TAG (8%) stop kodon (konten GC 50.8%).[9]
Substrat untuk stop kodon faktor pelepasan 1 atau faktor pelepasan 2 memiliki korelasi dengan kelimpahan stop kodon.[10] Skala besar studi tentang bakteri dengan berbagai kandungan GC menjelaskan bahwa frekuensi terjadinya TAA memiliki korelasi negatif dengan konten GC sementara frekuensi terjadinya TGA memiliki korelasi positif dengan konten GC, dan frekuensi terjadinya stop kodon TAG, menjadi paling sedikit dipakai dalam genom, dan tidak dipengaruhi oleh konten GC.[11]
Pengenalan
Pengenalan stop kodon terhadap bakteri telah dikaitkan dengan sebutan 'antikodon tripeptida',[12] motif asam amino yang sangat dilestarikan di RF1 (PxT) dan RF2 (SPF). Walaupun hal ini telah didukung oleh sebuah studi struktural, namun terbukti bahwa hipotesis antikodon tripeptida merupakan sebuah penyederhanaan yang berlebihan.[13]
Sistem pemberian istilah
Secara historis, stop kodon memiliki beragam nama yang berbeda, dan semuanya memiliki kaitan dengan kelas mutan yang berbeda namun semuanya berperilaku sama. Mutan ini terlebih dahulu diisolasi dalam bakteriofag (T4 dan lambda), virus yang menginfeksi bakteri Escherichia coli. Mutasi pada gen virus akan melemahkan kemampuan infeksi, dan ada kemungkinan akan menciptakan virus yang mampu menginfeksi dan tumbuh hanya dalam varietas E. coli tertentu.
Referensi
- ^ Griffiths AJF, Miller JH, Suzuki DT, Lewontin RC, Gelbart WM (2000). "Chapter 10 (Molecular Biology of Gene Function): Genetic code: Stop codons". An Introduction to Genetic Analysis. W.H. Freeman and Company.
- ^ Barrell, B. G.; Bankier, A. T.; Drouin, J. (1979-11-08). "A different genetic code in human mitochondria". Nature (dalam bahasa Inggris). 282 (5735): 189–194. doi:10.1038/282189a0. ISSN 0028-0836. PMID 226894.
- ^ A. M. Nedelcu, R. W. Lee, G. Lemieux, M. W. Gray, G. Burger (June 2000). "The complete mitochondrial DNA sequence of Scenedesmus obliquus reflects an intermediate stage in the evolution of the green algal mitochondrial genome". Genome Research. 10 (6): 819–831. doi:10.1101/gr.10.6.819. PMC 310893
 . PMID 10854413.
. PMID 10854413.
- ^ Wideman, Jeremy G.; Monier, Adam; Rodríguez-Martínez, Raquel; Leonard, Guy; Cook, Emily; Poirier, Camille; Maguire, Finlay; Milner, David S.; Irwin, Nicholas A. T.; Moore, Karen; Santoro, Alyson E. (2019-11-25). "Unexpected mitochondrial genome diversity revealed by targeted single-cell genomics of heterotrophic flagellated protists". Nature Microbiology (dalam bahasa Inggris). 5 (1): 154–165. doi:10.1038/s41564-019-0605-4. hdl:10871/39819
 . ISSN 2058-5276. PMID 31768028.
. ISSN 2058-5276. PMID 31768028.
- ^ Swart, Estienne Carl; Serra, Valentina; Petroni, Giulio; Nowacki, Mariusz (2016). "Genetic Codes with No Dedicated Stop Codon: Context-Dependent Translation Termination". Cell. 166 (3): 691–702. doi:10.1016/j.cell.2016.06.020. PMC 4967479
 . PMID 27426948.
. PMID 27426948.
- ^ Papp, Laura Vanda; Lu, Jun; Holmgren, Arne; Khanna, Kum Kum (2007). "From Selenium to Selenoproteins: Synthesis, Identity, and Their Role in Human Health". Antioxidants & Redox Signaling. 9 (7): 775–806. doi:10.1089/ars.2007.1528. PMID 17508906.
- ^ Povolotskaya IS, Kondrashov FA, Ledda A, Vlasov PK (2012). "Stop codons in bacteria are not selectively equivalent". Biology Direct. 7: 30. doi:10.1186/1745-6150-7-30. PMC 3549826
 . PMID 22974057.
. PMID 22974057.
- ^ Korkmaz, Gürkan; Holm, Mikael; Wiens, Tobias; Sanyal, Suparna (2014). "Comprehensive Analysis of Stop Codon Usage in Bacteria and Its Correlation with Release Factor Abundance". The Journal of Biological Chemistry. 289 (44): 775–806. doi:10.1074/jbc.M114.606632. PMC 4215218
 . PMID 25217634.
. PMID 25217634.
- ^ "Escherichia coli str. K-12 substr. MG1655, complete genome [Genbank Accession Number: U00096]". GenBank. NCBI. Diakses tanggal 2020-11-23.
- ^ Korkmaz, Gürkan; Holm, Mikael; Wiens, Tobias; Sanyal, Suparna (2014). "Comprehensive Analysis of Stop Codon Usage in Bacteria and Its Correlation with Release Factor Abundance". The Journal of Biological Chemistry. 289 (44): 775–806. doi:10.1074/jbc.M114.606632. PMC 4215218
 . PMID 25217634.
. PMID 25217634.
- ^ Wong, Tit-Yee; Fernandes, Sanjit; Sankhon, Naby; Leong, Patrick P; Kuo, Jimmy; Liu, Jong-Kang (2008). "Role of Premature Stop Codons in Bacterial Evolution". Journal of Bacteriology. 190 (20): 6718–6725. doi:10.1128/JB.00682-08. PMC 2566208
 . PMID 18708500.
. PMID 18708500.
- ^ Ito, Koichi; Uno, Makiko; Nakamura, Yoshikazu (1999). "A tripeptide 'anticodon' deciphers stop codons in messenger RNA". Nature. 403 (6770): 680–684. doi:10.1038/35001115. PMID 10688208.
- ^ Korkmaz, Gürkan; Sanyal, Suparna (2017). "R213I mutation in release factor 2 (RF2) is one step forward for engineering an omnipotent release factor in bacteria Escherichia coli". Journal of Biological Chemistry. 292 (36): 15134–15142. doi:10.1074/jbc.M117.785238. PMC 5592688
 . PMID 28743745.
. PMID 28743745.
